« Déterminer la structure 3D d'une protéine biologiquement importante » : différence entre les versions
m (ajouté des photos pour certaines protéines) |
|||
| (37 versions intermédiaires par 2 utilisateurs non affichées) | |||
| Ligne 4 : | Ligne 4 : | ||
Trouver quelques protéines pertinentes à vos cours | Trouver quelques protéines pertinentes à vos cours | ||
{| class="wikitable mw-collapsible mw-collapsed" | |||
|+NB: notes préalables | |||
| | |||
* pas toutes les structures 3D contiennent toutes les chaînes qui composent une macromolécule in vivo (exemple hémoglobine: beaucoup de structures 3D contiennent 2 chaînes au lieu des 4...) | |||
* pas toutes les structures 3D contiennent les ‘vraies’ chaînes qui composent une macromolécule in vivo (artéfact expérimental. Exemple hémoglobine : 4 x la même chaîne au lieu de 2 chaînes A et 2 chaînes B) | |||
* pas toutes les structures 3D ‘couvrent’ toute la longueur de la chaîne peptidique ! | |||
|} | |||
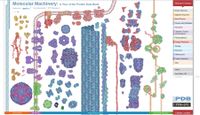
# choisir de préférence les structures 3D proposées à partir de ce poster MM PDB http://mm.rcsb.org/ | |||
*[[Fichier:Poster PDB proteines (thumb).jpg|alt=Poster PDB proteines (thumb)|centré|vignette|200x200px|Poster PDB proteines (thumb)]] | |||
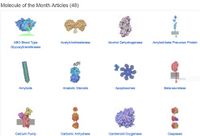
* pour les protéines avec médicaments : choisir les structures 3D proposées par PDB (à partir de ce poster) http://pdb101.rcsb.org/browse/you-and-your-health | |||
**[[Fichier:Poster de quelques protéines en lien avec la sante chez PDB.org.jpg|alt=Poster de quelques protéines en lien avec la santé chez PDB.org|centré|vignette|200x200px|Poster de quelques protéines en lien avec la santé chez PDB.org]]Sur PDB, on peut visualiser la protéine dans un viewer; sous le cadre de visualisation, choisir <small>Select a different viewer et</small> JSMOL qui nous parait être le plus adapté, selectionner l'option Space-filling | |||
== Nombreuses protéines avec leur structure et le fichier STL - prêtes pour impression == | |||
* Liste proposée au cours de formation continue PO 422 avec Dr. Marie-Claude Blatter du SIB | |||
* Liste proposée au cours de formation continue PO 422 avec | |||
** http://education.expasy.org/cours/PO422/PO422_Liste_3D.pdf | ** http://education.expasy.org/cours/PO422/PO422_Liste_3D.pdf | ||
{| class="wikitable" | {| class="wikitable" | ||
| Ligne 14 : | Ligne 23 : | ||
!Nom de la protéine ou du complexe | !Nom de la protéine ou du complexe | ||
!Lien vers UniProtKB/Swiss-Prot (section structure) | !Lien vers UniProtKB/Swiss-Prot (section structure) | ||
!Lien vers l’entrée PDB (PDB AC) | !Lien vers l’entrée PDB (PDB AC) | ||
Exemple de lien: https://www.rcsb.org/3d-view/5wrg | |||
!Photo | !Photo | ||
!Remarque | !Remarque | ||
! | !Fichiers .STL prêt à imprimer la plupart ajustées pour impression 3d par Julien Dacosta TECFA | ||
ou Bertrand Emery ([https://edu.ge.ch/site/fabrication-numerique/service-dimpression-3d/ SEM Fablab]) | |||
cf. exceptions dans le tableau | |||
|- Hémoglobine | |- Hémoglobine | ||
|Hemoglobine Humaine | |Hemoglobine Humaine | ||
| Ligne 25 : | Ligne 38 : | ||
2hhb | 2hhb | ||
| | |[[Fichier:Hemoglobine-3D-2hhb.jpg|alt=Hemoglobine complète imprimée en 3D à partir de 2hhb sur PDB (2x2 sous-unités en rouge groupements hème en blanc) |vignette|176x176px|Hemoglobine complète imprimée en 3D à partir de 2hhb sur PDB (2x2 sous-unités en rouge groupements hème en blanc) ]] | ||
| L’hémoglobine est constituée de 2 chaînes HBA et 2 chaînes HBB | | L’hémoglobine est constituée de 2 chaînes HBA et 2 chaînes HBB | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/hemoglobin-2HHB/Final/Hglobin150%25.stl Hemoglobin.stl] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/hemoglobin-2HHB/Final/Hglobin_Hemes150%25.stl Groupement Heme.stl] | |||
|- COX1 + aspirine ibuprofen | |- COX1 + aspirine ibuprofen | ||
|COX1 + aspirine COX1 + ibuprofen | |COX1 + aspirine COX1 + ibuprofen | ||
| Ligne 32 : | Ligne 47 : | ||
|1pth* | |1pth* | ||
1eqg | 1eqg | ||
| | |[[Fichier:Mains-inserent-COX-ibuprofen.jpg|alt=COX-1 imprimé en 3D à partir de PGH1 sur PDB - avec ibuprofen glissé entre les deux moitiés de la protéine |vignette|155x155px|COX-1 imprimé en 3D à partir de PGH1 sur PDB - avec ibuprofen glissé entre les deux moitiés de la protéine ]][[Fichier:Proteine Cox1 à partir de 1eqg sur PDB avec Ibuprofen -coupee .jpg|alt=Proteine Cox1 à partir de 1eqg sur PDB avec Ibuprofen -coupee |vignette|183x183px|Proteine Cox1 à partir de 1eqg sur PDB avec Ibuprofen -coupée ]] | ||
| | |Divers AINS (antidouleurs susceptibles de se fixer sur Cox1) | ||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Celecoxib.stl Celecoxib.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Diclofenac.stl Diclofenac.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Flurbiprofen.stl Flurbiprofen.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Ibuprofen.stl Ibuprofen.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Salicylic.stl Salicylic.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Nimesulid.stl Nimesulid] | |||
Fichiers fournis par Pr. Vincent Zoete, SIB Swiss Institute of Bioinformatics, University of Lausanne | |||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/COX1-Protein-only.stl COX1-Protein] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Salicylic.stl Acide salicylique] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Ibuprofen.stl Ibuprofen] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/cox1-et-ains-1EQG/Diclofenac.stl Diclofenac] | |||
|- Insuline | |- Insuline | ||
|Insuline Humaine | |Insuline Humaine | ||
|INS_HUMAN | |INS_HUMAN | ||
|2hiu* 1ben | |2hiu* 1ben | ||
| | |[[Fichier:Insuline.jpg|alt=Insuline imprimée en 3D à partir de 1A7 sur PDB - crayon pour l'échelle|vignette|200x200px|Insuline imprimée en 3D à partir de 1A7 sur PDB - crayon pour l'échelle]] | ||
|L’insuline est constituée de 2 chaînes (chaîne A : 21 aa, chaîne B : 30 aa). Dans l’entrée 2hiu, la chaîne B ne fait que 29 aa... | |L’insuline est constituée de 2 chaînes (chaîne A : 21 aa, chaîne B : 30 aa). Dans l’entrée 2hiu, la chaîne B ne fait que 29 aa... | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/insulin-1BEN/insuline-ready2print.stl InsulineReady2print.stl] | |||
|- Nucléosome | |- Nucléosome | ||
|Nucléosome ( humain) | |Nucléosome (humain) | ||
|H4_HUMAN | |H4_HUMAN | ||
|5b40 | |5b40 | ||
| | |[[Fichier:Histone-1-tourADN.jpg|alt=Nucleosome (histone + ADN) ) imprimé en 3D à partir de 5b40 sur PDB - normalement deux tours d'ADN |vignette|Nucleosome (histone + ADN) imprimé en 3D à partir de 5b40 sur PDB - normalement deux tours d'ADN |150x150px]] | ||
|La structure 3D contient les histones H4, H2A, H2B, H3.2 + ADN | |La structure 3D contient les histones H4, H2A, H2B, H3.2 + ADN | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/histone-complex-ADN-5b40/Final/5B40_histone-protein-only.stl 5B40_histone-protein-only.stl] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/histone-complex-ADN-5b40/Final/ADN-filament-enroule-2-tours_SOLID5.stl ADN-filament-enroule-2-tours_SOLID5.stl] | |||
|- Nucléosome | |- Nucléosome | ||
|Nucléosome (batracien) | |Nucléosome (batracien) | ||
| | |P62799 (H4_XENLA) | ||
|1aoi* | |1aoi* | ||
| | | | ||
| Ligne 58 : | Ligne 89 : | ||
|[[Fichier:1igy-immunoglobuline.jpg|alt=Immunoglobuline G imprimée en 3D à partir de 1igy sur PDB|vignette|267x267px|Immunoglobuline G imprimée en 3D à partir de 1igy sur PDB]] | |[[Fichier:1igy-immunoglobuline.jpg|alt=Immunoglobuline G imprimée en 3D à partir de 1igy sur PDB|vignette|267x267px|Immunoglobuline G imprimée en 3D à partir de 1igy sur PDB]] | ||
| 1igy | | | 1igy | | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/Immunoglobuline-IgG1/Final/IgG1-ready-2-print.stl.zip IgG1-ready-2-print.stl.zip] | |||
Version avec cavités pour aimants permettant de simuler l'affinité des poches antigéniques [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/Immunoglobuline-IgG1/Final/immunoglobine-IgG1-x2.stl (fichier imprimant 2 IgG1 tête-beche à la fois]) | |||
|- ATP synthase|ATPB_BOVIN | |- ATP synthase|ATPB_BOVIN | ||
|ATP Synthase | |ATP Synthase | ||
|ATPB_BOVIN | |ATPB_BOVIN | ||
| 5ara* | | 5ara* | ||
| | |[[Fichier:ATP synthase 3D printed.jpg|alt=ATP synthase 3D printed from 5 PDB ref ARA |centré|vignette|213x213px]] | ||
|Plusieurs sous-unités inclue ATP5B | |Plusieurs sous-unités inclue ATP5B | ||
Plus d’info : pdb101.rcsb.org/mot m/72 | Plus d’info : pdb101.rcsb.org/mot m/72 | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/ATPsynthase-5ARA/atp-synthase-probe1-vertex2.5-not-tested.stl.zip atp-synthase.stl.zip] | |||
|- tRNA | |- tRNA | ||
|tRNA | |tRNA | ||
| Ligne 72 : | Ligne 107 : | ||
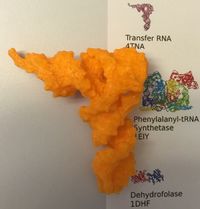
|[[Fichier:TRNA-3D-on-poster PDB.jpg|alt=Impression 3D de l'ARNt Phe sur le poster de PDB|vignette|209x209px|Impression 3D de l'ARNt Phe sur le poster de PDB]] | |[[Fichier:TRNA-3D-on-poster PDB.jpg|alt=Impression 3D de l'ARNt Phe sur le poster de PDB|vignette|209x209px|Impression 3D de l'ARNt Phe sur le poster de PDB]] | ||
|yeast tRNAPhe | |yeast tRNAPhe | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/ARN-transfer-4TNA/4TNA-ready2print.stl 4TNA-ready2print.stl] | |||
|- TP53 + DNA | |- TP53 + DNA | ||
|TP53 + DNA | |TP53 + DNA | ||
|P53_HUMAN | |P53_HUMAN | ||
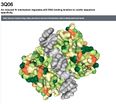
|3q06 | |3q06 | ||
| | |[[Fichier:3Q06-p53-onPDB.jpg|alt=Proteine P53 fixée sur l'ADN - a partir de 3Q06 sur PDB - vue dans PDB- pas imprimée|vignette|116x116px|Proteine P53 fixée sur l'ADN - a partir de 3Q06 sur PDB - vue dans PDB- pas imprimée]]Cf [https://www.rcsb.org/3d-view/jsmol/3q06 sur PDB] | ||
|393 aa : à l'heure de produire ce document aucune structure 3D ne couvre toute la séquence de la protéine | |393 aa : à l'heure de produire ce document aucune structure 3D ne couvre ''toute'' la séquence de la protéine | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/p53/3q06-p53-avec-ADN.stl P53-avec-ADN.stl] | |||
(encore pas testé à l'impression) | |||
|- RNA polymérase | |- RNA polymérase | ||
|RNA polymérase | |RNA polymérase | ||
| Ligne 84 : | Ligne 122 : | ||
| | | | ||
|Plusieurs sous-unités + DNA + RNA | |Plusieurs sous-unités + DNA + RNA | ||
| | |||
|- | |||
|Taq Polymérase | |||
|P19821 | |||
|1TAU | |||
|[[Fichier:1TAU-Taq-polymerase imprimée-3D.jpg|alt=Structure 3D de 1TAU dans PDB imprimée en 3D |vignette|267x267px|Structure 3D de 1TAU dans PDB imprimée en 3D ]] | |||
| | |||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/other/1TAU-Taq-polymerase.stl 1TAU-Taq-polymerase.stl] | |||
|- anthrax | |- anthrax | ||
| | |Amylase | ||
| | |P12070 | ||
| | |2die | ||
|[[Fichier:Structure 3D de l'Amylase à partir de 2die sur PDB.jpg|alt=Structure 3D de l'Amylase à partir de 2die sur PDB impression 3D|vignette|224x224px|Structure 3D de l'Amylase à partir de 2die sur PDB impression 3D]] | |||
| | | | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/other/2die-amylase.stl 2die-amylase.stl] | |||
|- GFP | |- GFP | ||
|Protéine fluorescente de méduse | |Protéine fluorescente de méduse | ||
| 1bfp |GFP_AEQVI | | 1bfp |GFP_AEQVI | ||
|1gfl | |1gfl | ||
| | |[[Fichier:GFP modele chaine et surface comparée .jpg|alt=Structure de la GFP à partir de PDB 1GFL modèle chaine et surface comparés|vignette|Structure de la GFP à partir de PDB 1GFL modèle chaine et surface comparées ]] | ||
|Séquence et structure complètes (blue GFP) | |Séquence et structure complètes (blue GFP) | ||
Green GFP | Green GFP | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/gfp-1GFL/1GFL_SingleChain-ribbon-thick.stl 1GFL_SingleChain-ribbon-thick.stl] | |||
Fichiers fournis par Romain Deweale | |||
|- Répresseur opéron lactose | |- Répresseur opéron lactose | ||
|Répresseur opéron lactose | |Répresseur opéron lactose | ||
| Ligne 102 : | Ligne 154 : | ||
| | | | ||
|Multimère de la même chaîne | |Multimère de la même chaîne | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/other/lactose-operon-repressor-1lbh.stl lactose-operon-repressor-1lbh.stl] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/1lbh-lactose_operon_repressor/1lbh-_lactose_operon_repressor_with_gratuitous_inducer_iptg.pdb 1lbh-_lactose_operon_repressor] | |||
|- ajouter la votre | |- ajouter la votre | ||
|CFTR | |CFTR | ||
| Ligne 112 : | Ligne 166 : | ||
|[[Fichier:CFTR-sain-printed.jpg|alt=CFTR - forme normale - imprimée en 3d à partir de 5uak sur PDB |vignette|292x292px|CFTR - forme normale - imprimée en 3d à partir de 5uak sur PDB]] | |[[Fichier:CFTR-sain-printed.jpg|alt=CFTR - forme normale - imprimée en 3d à partir de 5uak sur PDB |vignette|292x292px|CFTR - forme normale - imprimée en 3d à partir de 5uak sur PDB]] | ||
|cf. Scénario pour trouver la mutation la plus fréquente [[9) Éprouver comment on pourrait choisir les sondes pour déterminer un SNP spécifique ( la ∂F508 cause la plus fréquente de la mucoviscidose) dans une puce à ADN (µ-array)|la ∂F508 cause la plus fréquente de la mucoviscidose) dans une puce à ADN (µ-array)]] | |cf. Scénario pour trouver la mutation la plus fréquente [[9) Éprouver comment on pourrait choisir les sondes pour déterminer un SNP spécifique ( la ∂F508 cause la plus fréquente de la mucoviscidose) dans une puce à ADN (µ-array)|la ∂F508 cause la plus fréquente de la mucoviscidose) dans une puce à ADN (µ-array)]] | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/CFTR-sain/CFTR-ready-to-print.stl CFTR-ready-to-print.stl][[Fichier:CFTR-ready-to-print.stl|alt=Structure de CFTR - forme normale - convertie pour impression en 3d à partir de 5uak sur PDB|vignette|180x180px|Structure de CFTR convertie en.STL_pour impression en 3D à partir de 5uak sur PDB|néant]] | |||
|- | |||
|<nowiki/>CRISPR-Cas9 | |||
|Q99ZW2 | |||
|5F9R | |||
|[[Fichier:Cas9-5F9R-crispr-model 3D.jpg|alt=Protéine Cas9 en 3D à partir de la structure 5F9R sur PDB avec fermeture éclair comme modèle de l'ADN et l'ARN guide |vignette|160x160px|Protéine Cas9 en 3D à partir de la structure 5F9R sur PDB avec fermeture éclair comme modèle de l'ADN et l'ARN guide ]] | |||
|La fermeture éclair de taille grossière se trouve en mercerie ou récupérer sur un habit / sac. | |||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/5F9R-Cas9-DNA-primed-cleavage/Cas9-ready-to-print.stl Cas9-ready-to-print.stl] | |||
[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/5F9R-Cas9-DNA-primed-cleavage/cas9-crispr-printed-with-DNAzip-small.JPG cas9-crispr-printed-with-DNAzip-small.JPG] | |||
|- | |||
|Spike protein du virus SARS-Cov-2 | |||
|P0DTC2 | |||
|6VSB | |||
6VXX | |||
|[[Fichier:Spike-SARS-Cov-open-6VSB-SEMab.jpg|alt=Proteine Spike du virus SARS-Cov configuration ouverte - a partir de 6VSB sur PDB imprimee au -SEMab|vignette|170x170px|Proteine Spike du virus SARS-Cov configuration ouverte - a partir de 6VSB sur PDB imprimee au -SEMab]][https://media.nature.com/lw800/magazine-assets/d41586-020-02544-6/d41586-020-02544-6_18347822.gif image] | |||
|Cf.processus de fabrication [https://edu.ge.ch/site/fabrication-numerique/service-dimpression-3d/ SEMlab] | |||
[https://edu.ge.ch/site/fabrication-numerique/service-dimpression-3d/ Service d’impression 3D] | |||
| | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/spike-protein-6VSB-open/ready2print_6vsb-spike-protein-open.stl ready2print_6vsb-spike-protein-open.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/spike-protein-6VSB-open/ready2print_6vsb-spike-protein-openlight.stl ready2print_6vsb-spike-protein-openlight.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/spike-protein-6VXX-closed/ready2print_6VXX-spike-protein-closed.stl ready2print_6VXX-spike-protein-closed.stl] | |||
* [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/spike-protein-6VXX-closed/ready2print_6VXX-spike-protein-closed-light.stl ready2print_6VXX-spike-protein-closed-light.stl] | |||
|- | |||
|Récepteur à l'acétycholine- | |||
|P02711 | |||
|2bg9 | |||
|[[Fichier:2bg9 acétycholine-Receptor.jpg|alt=Récepteur à l'acétycholine imprimé en 3D à partir de la structure 2bg9 sur PDB|vignette|208x208px|Récepteur à l'acétycholine imprimé en 3D à partir de la structure 2bg9 sur PDB]] | |||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/acetycholine-recepteur-2bg9/recepteur-nicotiniques.MP4 recepteur-nicotiniques.MP4] | |||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/acetycholine-recepteur-2bg9/2bg9-acetycholine-recepteur.stl 2bg9-acetycholine-recepteur.stl] | |||
|- | |||
|Erythropoétine EPO | |||
|P01588 | |||
|1cn4 | |||
|[[Fichier:Erythropoiétine imprimée en 3D à partir de 1cn4 sur PDB.jpg|alt=Erythropoiétine imprimée en 3D à partir de 1cn4 sur PDB|vignette|204x204px|Erythropoiétine imprimée en 3D à partir de 1cn4 sur PDB]] | |||
| | | | ||
|[http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/other/1cn4-EPO.stl 1cn4-EPO.stl] | |||
|} | |} | ||
http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/ | [http://tecfa.unige.ch/perso/lombardf/formcont/proteines-3D/exemples-pdb-to-stl/ Grand répertoired'exemples-proteines-3d-stl/] | ||
Ces structures ont été choisies en collaboration entre Dr. M.C.Blatter du SIB et F. Lombard (IUFE TECFA) et imprimées par Julien Dacosta, Vincent Widmer, Stephane Morand de TECFA, coordonnés par Prof. Daniel K. Schneider TECFA. Bertand Emery au [https://edu.ge.ch/site/fabrication-numerique/service-dimpression-3d/ Service d’impression 3D] du SEMLab en a imprimé une partie. La COX1 et les AINS ont été fournis par Pr. Vincent Zoete, SIB Swiss Institute of Bioinformatics, University of Lausanne | |||
==Exemples de questions pour TP de biologie / pour s’en inspirer == | ==Exemples de questions pour TP de biologie / pour s’en inspirer == | ||
| Ligne 126 : | Ligne 220 : | ||
* Comment la forme constatée détermine-t-elle l’activité de la protéine ? | * Comment la forme constatée détermine-t-elle l’activité de la protéine ? | ||
* Comparez la séquence sur UniProtKB, puis la forme 3D pour diverses protéines: | * Comparez la séquence sur UniProtKB, puis la forme 3D pour diverses protéines: | ||
** Insuline ( http://www.rcsb.org/structure/1ben ) | ** Insuline (http://www.rcsb.org/structure/1ben ; alternative (avec la séquence de la protéine: https://www.rcsb.org/3d-view/1ben/)) | ||
** Immunoglobuline IgG ( http://www.rcsb.org/structure/1igy) | ** Immunoglobuline IgG ( http://www.rcsb.org/structure/1igy; alternative (avec la séquence de la protéine: [https://www.rcsb.org/3d-view/1igy https://www.rcsb.org/3d-view/1igy/])) | ||
* Quelles parties de la forme de l’hormone, l’anticorps semble être en rapport avec leur fonction ? | * Quelles parties de la forme de l’hormone, l’anticorps semble être en rapport avec leur fonction ? | ||
* La forme détermine-t-elle seule la fonction ? | * La forme détermine-t-elle seule la fonction ? | ||
| Ligne 133 : | Ligne 227 : | ||
* Pour ces deux protéines, quelles parties de la protéine pourraient – à votre avis - changer un peu suite à une mutation sans gravement mettre en cause son fonctionnement et finalement réduire la fécondité de l'animal qui a ce génome-là ? | * Pour ces deux protéines, quelles parties de la protéine pourraient – à votre avis - changer un peu suite à une mutation sans gravement mettre en cause son fonctionnement et finalement réduire la fécondité de l'animal qui a ce génome-là ? | ||
* Pour quelles autres parties un changement risque-t-il de nuire au fonctionnement de la protéine ? | * Pour quelles autres parties un changement risque-t-il de nuire au fonctionnement de la protéine ? | ||
** Idem pour l’histone | ** Idem pour l’histone HIST1H4A | ||
** Idem pour l’insuline INS | ** Idem pour l’insuline INS | ||
** Idem pour le récepteur à la mélanotropine MC1R | ** Idem pour le récepteur à la mélanotropine MC1R | ||
* Concluez sur le lien entre forme et fonction, les limites du modèle « clé- serrure » | * Concluez sur le lien entre forme et fonction, les limites du modèle « clé- serrure » | ||
== '' | == ''Liens externes '' == | ||
* [https://edu.ge.ch/site/fabrication-numerique/service-dimpression-3d/ Service d’impression 3D] au SEMLab : dédié au DIP | |||
== Scénarios pédagogiques où il peut s'intégrer == | |||
Ce scénario s'inscrit particulièrement bien après le scénario : [[Preuve de l'évolution par la comparaison de protéines chez différentes espèces]] | |||
On peut continuer avec ce scénario pour [[Convertir la structure de la protéine en fichier pour imprimante 3D]](.STL) | |||
* | |||
== | == Références == | ||
Scénario établi en partie sur la base des indications scientifiques de M.-C. Blatter du SIB | |||
Les plupart des fichiers .STL ont été optimisés pour l'impression par Julien Dacosta et aussi Vincent Widmer, Stephane Morand (TECFA), sauf : la GFP par Romain Deweale. | |||
La COX1 et les AINS ont été fournis par Pr. Vincent Zoete, SIB Swiss Institute of Bioinformatics, University of Lausanne | |||
Retour à [[Bioinformatique : opportunités pour l’enseignement]] | Retour à [[Bioinformatique : opportunités pour l’enseignement]] | ||
[[Catégorie: BioInfoScenarios]] | [[Catégorie: BioInfoScenarios]] | ||
Dernière version du 27 février 2024 à 12:20
Déterminer la structure 3D d'une protéine biologiquement importante
Procédure
Trouver quelques protéines pertinentes à vos cours
|
- choisir de préférence les structures 3D proposées à partir de ce poster MM PDB http://mm.rcsb.org/
- pour les protéines avec médicaments : choisir les structures 3D proposées par PDB (à partir de ce poster) http://pdb101.rcsb.org/browse/you-and-your-health
- Sur PDB, on peut visualiser la protéine dans un viewer; sous le cadre de visualisation, choisir Select a different viewer et JSMOL qui nous parait être le plus adapté, selectionner l'option Space-filling
Nombreuses protéines avec leur structure et le fichier STL - prêtes pour impression
- Liste proposée au cours de formation continue PO 422 avec Dr. Marie-Claude Blatter du SIB
| Nom de la protéine ou du complexe | Lien vers UniProtKB/Swiss-Prot (section structure) | Lien vers l’entrée PDB (PDB AC)
Exemple de lien: https://www.rcsb.org/3d-view/5wrg |
Photo | Remarque | Fichiers .STL prêt à imprimer la plupart ajustées pour impression 3d par Julien Dacosta TECFA
ou Bertrand Emery (SEM Fablab) cf. exceptions dans le tableau |
|---|---|---|---|---|---|
| Hemoglobine Humaine | HBB_HUMAN HBA_HUMAN | 1a00
4hhb* 2hhb |
L’hémoglobine est constituée de 2 chaînes HBA et 2 chaînes HBB | Hemoglobin.stl | |
| COX1 + aspirine COX1 + ibuprofen | PGH1_SHEEP | 1pth*
1eqg |
Divers AINS (antidouleurs susceptibles de se fixer sur Cox1)
Fichiers fournis par Pr. Vincent Zoete, SIB Swiss Institute of Bioinformatics, University of Lausanne |
COX1-Protein | |
| Insuline Humaine | INS_HUMAN | 2hiu* 1ben | L’insuline est constituée de 2 chaînes (chaîne A : 21 aa, chaîne B : 30 aa). Dans l’entrée 2hiu, la chaîne B ne fait que 29 aa... | InsulineReady2print.stl | |
| Nucléosome (humain) | H4_HUMAN | 5b40 | La structure 3D contient les histones H4, H2A, H2B, H3.2 + ADN | 5B40_histone-protein-only.stl | |
| Nucléosome (batracien) | P62799 (H4_XENLA) | 1aoi* | H4, H2B11, H33C, H2A1 + ADN | ||
| Immuno-globuline IgG | GCAA_MOUSE IGH1M_MOUSE | 1igt* 1igy | IgG1-ready-2-print.stl.zip
Version avec cavités pour aimants permettant de simuler l'affinité des poches antigéniques (fichier imprimant 2 IgG1 tête-beche à la fois) | ||
| ATP Synthase | ATPB_BOVIN | 5ara* | Plusieurs sous-unités inclue ATP5B
Plus d’info : pdb101.rcsb.org/mot m/72 |
atp-synthase.stl.zip | |
| tRNA | N'est pas une protéine ! | 4tna | yeast tRNAPhe | 4TNA-ready2print.stl | |
| TP53 + DNA | P53_HUMAN | 3q06 | Cf sur PDB | 393 aa : à l'heure de produire ce document aucune structure 3D ne couvre toute la séquence de la protéine | P53-avec-ADN.stl
(encore pas testé à l'impression) |
| RNA polymérase | RPAB4_YEAST | 2e2i* | Plusieurs sous-unités + DNA + RNA | ||
| Taq Polymérase | P19821 | 1TAU | 1TAU-Taq-polymerase.stl | ||
| Amylase | P12070 | 2die | 2die-amylase.stl | ||
| Protéine fluorescente de méduse | GFP_AEQVI | 1gfl | Séquence et structure complètes (blue GFP)
Green GFP |
1GFL_SingleChain-ribbon-thick.stl
| |
| Répresseur opéron lactose | LACI_ECOLI | 1lbh | Multimère de la même chaîne | lactose-operon-repressor-1lbh.stl | |
| CFTR
Protéine dont le défaut cause la mucoviscidose |
CFTR_HUMAN
P13569 |
5uak | cf. Scénario pour trouver la mutation la plus fréquente la ∂F508 cause la plus fréquente de la mucoviscidose) dans une puce à ADN (µ-array) | CFTR-ready-to-print.stl | |
| CRISPR-Cas9 | Q99ZW2 | 5F9R | La fermeture éclair de taille grossière se trouve en mercerie ou récupérer sur un habit / sac. | Cas9-ready-to-print.stl | |
| Spike protein du virus SARS-Cov-2 | P0DTC2 | 6VSB
6VXX |
image
|
Cf.processus de fabrication SEMlab | |
| Récepteur à l'acétycholine- | P02711 | 2bg9 | recepteur-nicotiniques.MP4 | 2bg9-acetycholine-recepteur.stl | |
| Erythropoétine EPO | P01588 | 1cn4 | 1cn4-EPO.stl |
Grand répertoired'exemples-proteines-3d-stl/
Ces structures ont été choisies en collaboration entre Dr. M.C.Blatter du SIB et F. Lombard (IUFE TECFA) et imprimées par Julien Dacosta, Vincent Widmer, Stephane Morand de TECFA, coordonnés par Prof. Daniel K. Schneider TECFA. Bertand Emery au Service d’impression 3D du SEMLab en a imprimé une partie. La COX1 et les AINS ont été fournis par Pr. Vincent Zoete, SIB Swiss Institute of Bioinformatics, University of Lausanne
Exemples de questions pour TP de biologie / pour s’en inspirer
- On dit parfois que la séquence d’acides aminés (a.a) détermine la fonction de la protéine. En quoi est-ce correct et en quoi cela est-il incomplet ?
- Comment la structure secondaire et tertiaire est-elle établie avec ce que vous avez pu voir jusqu’ici ? ( dans quels organites ? Comment ?)
- Peut-on actuellement prédire la forme que prendra une protéine à partir de sa séquence ?
- Comment détermine-t-on la forme que prend effectivement une protéine ?
- Comment la forme constatée détermine-t-elle l’activité de la protéine ?
- Comparez la séquence sur UniProtKB, puis la forme 3D pour diverses protéines:
- Insuline (http://www.rcsb.org/structure/1ben ; alternative (avec la séquence de la protéine: https://www.rcsb.org/3d-view/1ben/))
- Immunoglobuline IgG ( http://www.rcsb.org/structure/1igy; alternative (avec la séquence de la protéine: https://www.rcsb.org/3d-view/1igy/))
- Quelles parties de la forme de l’hormone, l’anticorps semble être en rapport avec leur fonction ?
- La forme détermine-t-elle seule la fonction ?
- Essayez de déterminer comment la forme d’un anticorps Ig détermine sa fonction ?
- Pour ces deux protéines, quelles parties de la protéine pourraient – à votre avis - changer un peu suite à une mutation sans gravement mettre en cause son fonctionnement et finalement réduire la fécondité de l'animal qui a ce génome-là ?
- Pour quelles autres parties un changement risque-t-il de nuire au fonctionnement de la protéine ?
- Idem pour l’histone HIST1H4A
- Idem pour l’insuline INS
- Idem pour le récepteur à la mélanotropine MC1R
- Concluez sur le lien entre forme et fonction, les limites du modèle « clé- serrure »
Liens externes
- Service d’impression 3D au SEMLab : dédié au DIP
Scénarios pédagogiques où il peut s'intégrer
Ce scénario s'inscrit particulièrement bien après le scénario : Preuve de l'évolution par la comparaison de protéines chez différentes espèces
On peut continuer avec ce scénario pour Convertir la structure de la protéine en fichier pour imprimante 3D(.STL)
Références
Scénario établi en partie sur la base des indications scientifiques de M.-C. Blatter du SIB
Les plupart des fichiers .STL ont été optimisés pour l'impression par Julien Dacosta et aussi Vincent Widmer, Stephane Morand (TECFA), sauf : la GFP par Romain Deweale.
La COX1 et les AINS ont été fournis par Pr. Vincent Zoete, SIB Swiss Institute of Bioinformatics, University of Lausanne