« SNP fréquents - changements d'une seule base » : différence entre les versions
Aller à la navigation
Aller à la recherche
m (mise en page mineure) |
mAucun résumé des modifications |
||
| Ligne 19 : | Ligne 19 : | ||
== Scénarios pédagogiques où il peut s'intégrer == | == Scénarios pédagogiques où il peut s'intégrer == | ||
* | |||
===== Références ===== | |||
Scénario établi en partie sur la base des indications scientifiques de M.-C. Blatter du SIB | |||
Retour à [[Bioinformatique : opportunités pour l’enseignement]] | Retour à [[Bioinformatique : opportunités pour l’enseignement]] | ||
[[Catégorie: BioInfoScenarios]] | [[Catégorie: BioInfoScenarios]] | ||
Version du 1 octobre 2021 à 16:39
Éprouver que les SNP sont fréquents et sont des changements d'une seule base par exemple dans le gène CFTR
Procédure
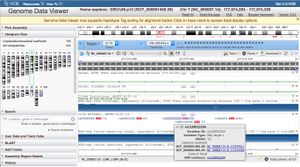
Ouvrir Genome data Viewer GDV ici
Préalable trouver une séquence d'un gène : Séquence du gène de protéines sur chromosomes
- Afficher la séquence d'une protéine à choix : p. ex CFTR
- [Solution]
- Si nécessaire zoomer à la séquence (icone ATG),
- Observer les SNP en bleu noter leur fréquence
- En choisir un (par exemple rs1228922204)
- -> cliquer sur le SNP choisi [solution]
- Repérer la base qui change T<->C dans ce cas
Ce qu'on peut obtenir : p. ex, synthèse par un élève des résultats avec une classe
Scénarios pédagogiques où il peut s'intégrer
Références
Scénario établi en partie sur la base des indications scientifiques de M.-C. Blatter du SIB