« Limite introns-exons pas discernable » : différence entre les versions
Aller à la navigation
Aller à la recherche
(Création de la page) |
(procédure) |
||
| Ligne 2 : | Ligne 2 : | ||
== Procédure == | == Procédure == | ||
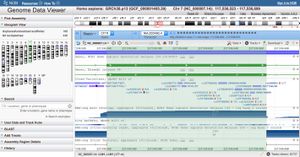
Ouvrir Genome data Viewer GDV [https://www.ncbi.nlm.nih.gov/genome/gdv/ ici] | Ouvrir Genome data Viewer GDV [https://www.ncbi.nlm.nih.gov/genome/gdv/ ici][[Fichier:CFTR gene Exon7 highlith in GDV.jpg|alt=CFTR gene Exon7 highlith in GDV|vignette|CFTR gene Exon7 highlith in GDV|lien=https://edutechwiki.unige.ch/fr/Fichier:CFTR_gene_Exon7_highlith_in_GDV.jpg]] | ||
*Sélectionner un gène (p. ex CFTR) selon protocole ([https://www.ncbi.nlm.nih.gov/genome/gdv/browser/blast/?cfg=NCID_1_32903492_130.14.18.128_9146_1584116293_2168709450 solution]) | |||
*Observer les bandes bleues plus bas sous ''RNAseq exon coverage'' et ''RNAseq intron spanning read'' | |||
*Chercher à voir si la limite est bien distincte ou si il y a des zones qui sont parfois exprimées comme exons ou non. | |||
*Discuter de l'épissage alternatif | |||
== ''Ce qu'on peut obtenir : p. ex, synthèse par un élève des résultats avec une classe '' == | == ''Ce qu'on peut obtenir : p. ex, synthèse par un élève des résultats avec une classe '' == | ||
Synthèse d'un élève : La limite introns-exons est difficilement discernable car sur le graphique, on n'observe qu’une partie des exons déborde sur une partie des introns, il est donc compliqué d’apercevoir une limite car celle-ci n’est pas clair et bien délimitée. On éprouve donc que les introns peuvent être des exons et les exons peuvent être des introns en fonction de la protéine produite. Avec l’épissage alternatif, la limite introns-exons est donc minime. | |||
== Scénarios pédagogiques où il peut s'intégrer == | == Scénarios pédagogiques où il peut s'intégrer == | ||
A faire encore | |||
---- | ---- | ||
Retour à [[Bioinformatique : opportunités pour l’enseignement]] | Retour à [[Bioinformatique : opportunités pour l’enseignement]] | ||
[[Catégorie: BioInfoScenarios]] | [[Catégorie: BioInfoScenarios]] | ||
Version du 20 mars 2020 à 17:20
Éprouver que la limite introns-exons n'est pas discernable aisément.
Procédure
Ouvrir Genome data Viewer GDV ici
- Sélectionner un gène (p. ex CFTR) selon protocole (solution)
- Observer les bandes bleues plus bas sous RNAseq exon coverage et RNAseq intron spanning read
- Chercher à voir si la limite est bien distincte ou si il y a des zones qui sont parfois exprimées comme exons ou non.
- Discuter de l'épissage alternatif
Ce qu'on peut obtenir : p. ex, synthèse par un élève des résultats avec une classe
Synthèse d'un élève : La limite introns-exons est difficilement discernable car sur le graphique, on n'observe qu’une partie des exons déborde sur une partie des introns, il est donc compliqué d’apercevoir une limite car celle-ci n’est pas clair et bien délimitée. On éprouve donc que les introns peuvent être des exons et les exons peuvent être des introns en fonction de la protéine produite. Avec l’épissage alternatif, la limite introns-exons est donc minime.
Scénarios pédagogiques où il peut s'intégrer
A faire encore